Glossário - Temas de Genética (ATUALIZADO)
PRORROGAÇÃO DO PRAZO:
Neste novo glossário vocês devem adicionar os seus respectivos temas e definições, juntamente com as referências bibliográficas (preferencialmente de livros de Genética).
Prazo: 23/05, ás 18:00h.
A | B | C | D | E | F | G | H | I | J | K | L | M | N | O | P | Q | R | S | T | U | V | W | X | Y | Z | Todos
Critério de ordenação atual: Nome crescente Ordenar por: Sobrenome | Nome
JBJulia Buzatto da Silva |
|---|
| JB | Histona | |||
|---|---|---|---|---|
Histona Histonas são proteínas associadas com o DNA nos cromossomos, ricas em aminoácidos básicos (lisina ou arginina) e praticamente em variação ao longo da evolução eucariótica. Ligações covalentes das histonas são importantes reguladores epigenéticos da expressão gênica. O padrão de histonas e suas modificações constituem o “código epigenético de histonas”.
Referência bibliográfica: Thompson & Thompson Genética Médica - 8ª Edição | ||||
| JB | Homologia | |||
|---|---|---|---|---|
Homologia Homologia é um termo comumente utilizado em genética, mas com significados diferentes em contextos diferentes. 1. Em bioinformática, sequências homólogas são sequências de DNA ou de proteínas que possuem sequências nucleotídicas ou de aminoácidos semelhantes, como pode ser visto entre genes ortólogos ou parálogos. 2. Na citogenética, cromossomos homólogos são um par de cromossomos em que um é herdado paternalmente e o outro é de origem materna. Geralmente têm tamanho e formatos semelhantes, quando vistos sob o microscópio, e contêm os mesmos loci, exceto os dois cromossomos sexuais (X e Y) nos homens, que são parcialmente homólogos. Cromossomos homólogos se emparelham durante a meiose I e sofrem o “crossing over”, sendo separados na anáfase I da meiose. 3. Na evolução, estruturas em diferentes organismos são denominadas homólogas se evoluíram de uma estrutura presente em um ancestral comum.
Referência bibliográfica: Thompson & Thompson Genética Médica - 8ª Edição | ||||
| JB | Homozigoto | |||
|---|---|---|---|---|
Homozigoto É o indivíduo ou genótipo com alelos idênticos para um locus determinado num par de cromossomos homólogos.
Referência bibliográfica: Thompson & Thompson Genética Médica - 8ª Edição | ||||
JEJulia Elisa Francisco |
|---|
| JE | Integração Viral (137) | |||
|---|---|---|---|---|
A integração viral faz parte do ciclo de replicação do vírus e corresponde ao processo em que o material genético do vírus é inserido no genoma de uma célula hospedeira. A partir do momento em que o material genético viral é integrado, ele poderá ser replicado junto com o DNA da célula hospedeira, o que resulta na produção contínua do vírus.A exemplo disso, é possível citar a integração do DNA retroviral (HIV) com o DNA celular. O HIV é um retrovírus, portanto seu genoma é constituído por RNA e é convertido em DNA através da ação da transcriptase reversa, após esse processo o material genético viral é integrado ao DNA do hospedeiro utilizando a enzima integrase viral, o que permite a replicação do vírus junto com o DNA celular.
Referências Bibliográficas: Livro HIV/AIDS-Associated Viral Oncogenesis. (2018). Alemanha: Springer International Publishing. Descritores em Ciências da Saúde: DeCS. 2023. ed. rev. e ampl. São Paulo: BIREME / OPAS / OMS, 2023. Disponível em: < http://decs.bvsalud.org/ >
| ||||
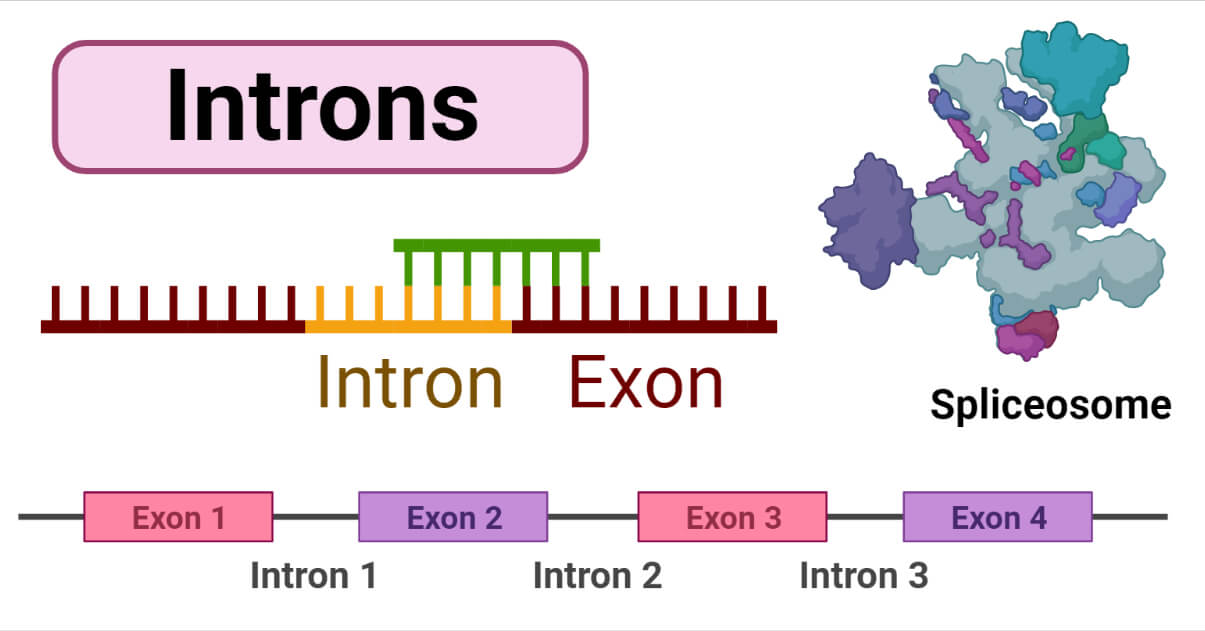
| JE | Introns (138) | |||
|---|---|---|---|---|
Os íntrons são sequências de bases nitrogenadas presentes no DNA que se intercalam com os éxons. Contudo, durante o processo de transcrição os íntrons são removidos naturalmente, de forma que nâo compõem o RNA mensageiro. Os íntrons são importantes para a regular a expressão gênica o que contribui para a diversidade genética.
Referências Bibliográficas: Pasternak, J. J. (2002). Genética molecular humana. Brasil: MANOLE. McInnes, R. R., Willard, H. F., Nussbaum, R. (2016). Thompson & Thompson Genética Médica. Brasil: Elsevier Editora Ltda.. | ||||
| JE | Inversão Cromossômica (139) | |||
|---|---|---|---|---|
A inverção cromossômica é uma forma de alteração estrutural dos cromossomos em que há a separação de uma parte do cromossomo e posteriormente a união dessa mesma porção, mas de forma invertida. Assim, a inversão não provoca alterações no número de genes, porém muda a posição dos genes presentes no cromossomo, o que afeta a forma como esse genes são expressos.  Referências Bibliográficas: Livro Pasternak, J. J. (2002). Genética molecular humana. Brasil: MANOLE. McInnes, R. R., Willard, H. F., Nussbaum, R. (2016). Thompson & Thompson Genética Médica. Brasil: Elsevier Editora Ltda.. | ||||
| JE | Ligação Gênica (140) | |||
|---|---|---|---|---|
Ligação gênica (140)A ligação gênica, também chamada de linkage, corresponde a presença de dois ou mais genes em um mesmo cromossomo. Tais genes, dependendo da distância em que se encontram uns dos outros no cromossomo podem continuar unidos durante a formação dos gametas, sendo transmitidos em conjunto durante a meiose ou podem se separar por recombinação gênica. A ligação gênica pode ser completa, quando não ocorre recombinação, ou, incompleta quando há recombinação gênica.
Referência Bibliográfica: Livro Watson, J. D., Baker, T. A., Bell, S. P., Gann, A., Levine, M. (2015). Biologia Molecular do Gene - 7ed. Brasil: Artmed Editora. | ||||
JLJúlia Limberti Gomes |
|---|
| JL | Ligase | |||
|---|---|---|---|---|
É uma enzima envolvida na duplicação do DNA e promove a ligação entre os nucleotídeos de duas moléculas, uma vez que é essencial para essa síntese. DNA ligase é uma enzima de adesão de DNA. Se dois pedaços de DNA tiverem terminações complementares, a ligase pode ligá-las para formar uma molécula de DNA única e contínua. Referência: https://pt.khanacademy.org/science/biology/biotech-dna-technology/dna-cloning-tutorial/a/restriction-enzymes-dna-ligase#:~:text=DNA%20ligase%20%C3%A9%20uma%20enzima,de%20DNA%20%C3%BAnica%20e%20cont%C3%ADnua. | ||||
| JL | Locus | |||
|---|---|---|---|---|
Posição ocupada pelo gene no cromossomo. Formas diferentes de genes (alelos) podem ocupar o locus. Referência: Thompson & Thompson Genética Médica https://g.co/kgs/ZB6paCp | ||||
| JL | Long non coding RNA | |||
|---|---|---|---|---|
RNA não codificante longo (lncRNAs), que são definidos como RNA com mais de 200 nt de comprimento, mas sem capacidade de codificação de proteínas, é cada vez mais enfatizado devido à sua função biológica. No genoma dos mamíferos, mais de 1000 nt de grandes RNAs intergênicos não codificantes (lnc) são claramente conservados em diferentes mamíferos e, portanto, seus padrões funcionais e de expressão gênica implicaram que esses lncRNAs auxiliam em diversos processos biológicos, incluindo regulação do ciclo celular, vigilância imunológica e pluripotência de células-tronco embrionárias. Referência: https://www.ncbi.nlm.nih.gov/pmc/articles/PMC10149988/ | ||||